本文介绍吉林大学李向涛教授课题组发表在AAAI 2022上的一篇论文“ZINB-based Graph Embedding Autoencoder for Single-cell RNA-seq Interpretations”。作者提出了一种基于单细胞模型的深度图嵌入聚类,称为scTAG,它将零膨胀负二项式模型集成到拓扑自适应图卷积自编码器中。scTAG 构建细胞图并使用拓扑自适应图卷积自动编码器来共同保存 scRNA-seq 数据中的拓扑结构信息和细胞间关系。
文章地址:
https://www.aaai.org/AAAI22Papers/AAAI-5060.YuZ.pdf
代码地址:
https://github.com/Philyzh8/scTAG
摘要:
单细胞RNA 测序(scRNA-seq)以单细胞分辨率提供有关全基因组基因表达水平的高通量信息,从而准确了解单个细胞的转录组。然而,快速增长的scRNA-seq数据和普遍存在的dropout 事件给细胞类型注释带来了巨大挑战。作者提出了一种基于单细胞模型的深度图嵌入聚类方法(scTAG),该方法同时学习细胞-细胞拓扑表示并基于深度图卷积网络识别细胞簇。scTAG将零膨胀负二项式(ZINB)模型集成到拓扑自适应图卷积自编码器中,以学习低维潜在表示,并采用 Kullback-Leibler(KL)散度进行聚类任务。通过同时优化聚类损失、ZINB 损失和单元图重建损失,scTAG联合优化了聚类标签分配和特征学习,并以端到端的方式保留了拓扑结构。对来自不同但具有代表性的单细胞测序平台的16个单细胞 RNA-seq 数据集进行的广泛实验证明了 scTAG 优于各种最先进的聚类方法。
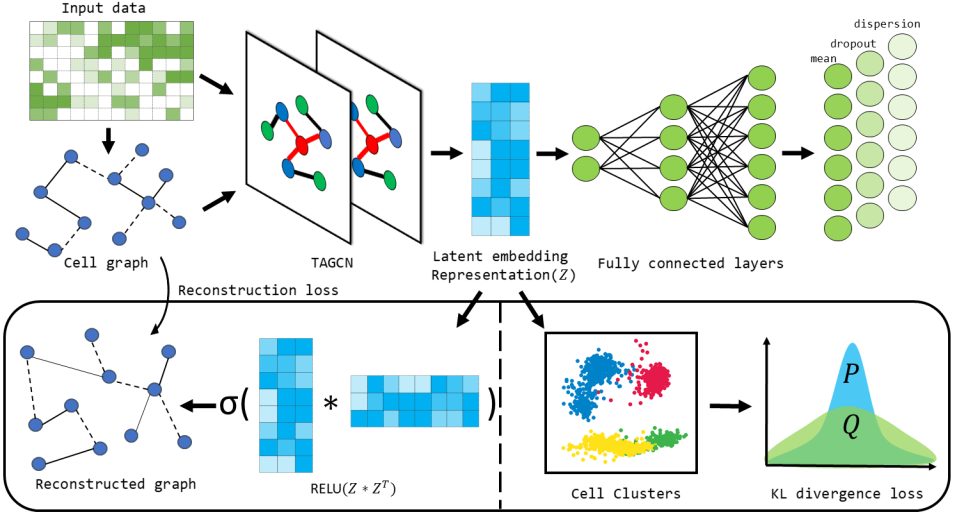 Overview of scTAG
Overview of scTAG
内容中包含的图片若涉及版权问题,请及时与我们联系删除



评论
沙发等你来抢