【标题】De novo design of protein target specific scaffold-based Inhibitors via Reinforcement Learning
【作者团队】Andrew D. McNaughton, Mridula S. Bontha, Carter R. Knutson, Jenna A. Pope, Neeraj Kumar
【发表日期】2022.5.21
【论文链接】https://arxiv.org/pdf/2205.10473.pdf
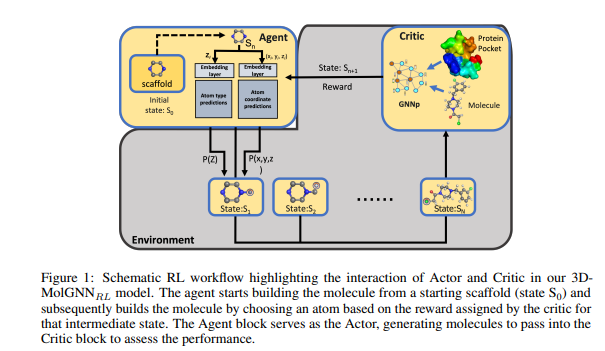
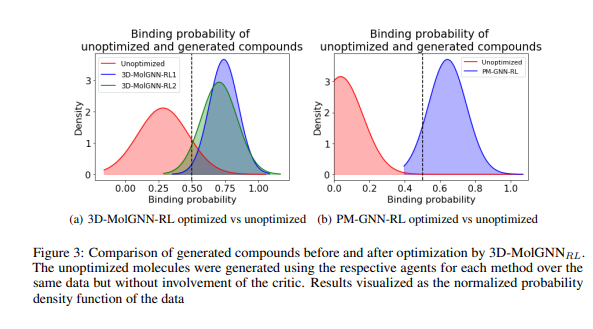
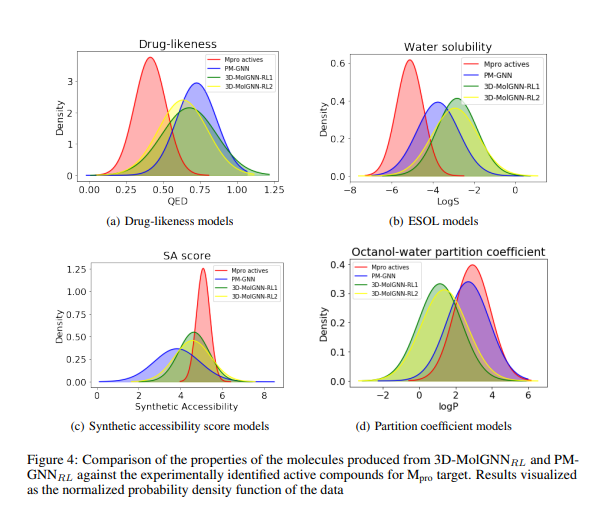
【推荐理由】靶向驱动分子的有效设计和发现是促进药物发现中铅优化的关键步骤。目前研究靶蛋白分子的方法是直觉驱动的,由于利用3D结构数据的计算挑战,迭代设计测试周期缓慢,最终受到化学家专业知识的限制,从而导致分子设计的瓶颈。本文提出了一个新的框架,称为3D MolGNNRL,将强化学习(RL)耦合到基于3D支架的深度生成模型,以生成针对从起始核心支架逐原子构建的蛋白质的靶候选。3D MolGNNRL提供了一种利用并行图神经网络模型通过蛋白质口袋内的多目标奖励函数优化关键特征的有效方法。该试剂学习在3D空间中构建分子,同时优化针对传染病蛋白质靶点生成的候选物的活性、结合亲和力、效力和合成可及性。该方法可以作为一种可解释的人工智能(AI)工具,用于优化铅的活性、效力和生物物理特性。
内容中包含的图片若涉及版权问题,请及时与我们联系删除



评论
沙发等你来抢