Uni-Dock 是由深势科技开发的高性能分子对接软件,能在 GPU 上以超过单 CPU 千倍的速度完成虚拟筛选任务。2023 年 6 月,Uni-Dock 以封面文章形式发表在 JCTC 杂志上[1];同年 8 月,Uni-Dock 加入 DeepModeling 社区,在 LGPL 协议下开放源代码,并发布 v1.0 版本。在过去的半年中,Uni-Dock 得到了学术界和工业界的关注、支持和应用。Uni-Dock 已实践于多个早期药物发现项目,被多个软件平台集成和收录,并为药物设计领域的 AI for Science 方法开发提供了高效的数据标记、评估和预测的能力。Uni-Dock 已经成为药物研发工作者和 AI for Science 方法开发者的优选工具。作为 DeepModeling 社区的孵化软件,Uni-Dock 以开放的姿态拥抱开源社区。广大用户的使用反馈和开源社区开发者的贡献,共同推动了 Uni-Dock 的持续优化和进步,Uni-Dock 的开源协作模式也随着软件迭代过程变得更加明确和规范。2024年2月,Uni-Dock 发布 v1.1 版本。新版本合并了近半年以来,包括深势科技、NVIDIA 等在内的开发者贡献的众多新特性,分子对接和虚拟筛选效率进一步提升;同时,Uni-Dock Tools 工具包的发布为广大用户带来了更好的使用体验和优秀的实践案例;另外,新版本中发布了 Uni-Dock Benchmarks 基准测试集、完善了 Uni-Dock CI/CD 流程等开发套件,并明确了 Uni-Dock 的开源协作模式,为更广泛的开源合作提供了基础。Uni-Dock v1.1 代码可从以下 GitHub 仓库获取:https://github.com/dptech-corp/Uni-Dock/releases/tag/1.1.0


Uni-Dock 的 LOGO 标识为一个戴着帽子的吃豆人的形象延展,由青色的配体分子、蓝色的受体蛋白和紫色的筛选漏斗组成,展现了 Uni-Dock 在虚拟筛选过程中的主要元素。Uni-Dock v1.1
更快的分子对接、更快的虚拟筛选
Uni-Dock v1.1 在分子对接和虚拟筛选的计算效率上得到了进一步的显著提升。
分子对接特指单个配体分子向单个受体蛋白的对接计算过程,常常用于受体蛋白-配体分子结合复合物的结构预测,以获得两者的结合模式来开展相互作用分析,指导理性药物设计。在 Uni-Dock v1.1 版本中,分子对接的主要提升如下:
- 实现了单配体单分子对接计算模式:在原有的单配体多分子的计算流程基础上,使用 CUDA stream 轻量化地实现 1:1 docking 的快速计算,并提供了相关计算案例与配置文件结构。
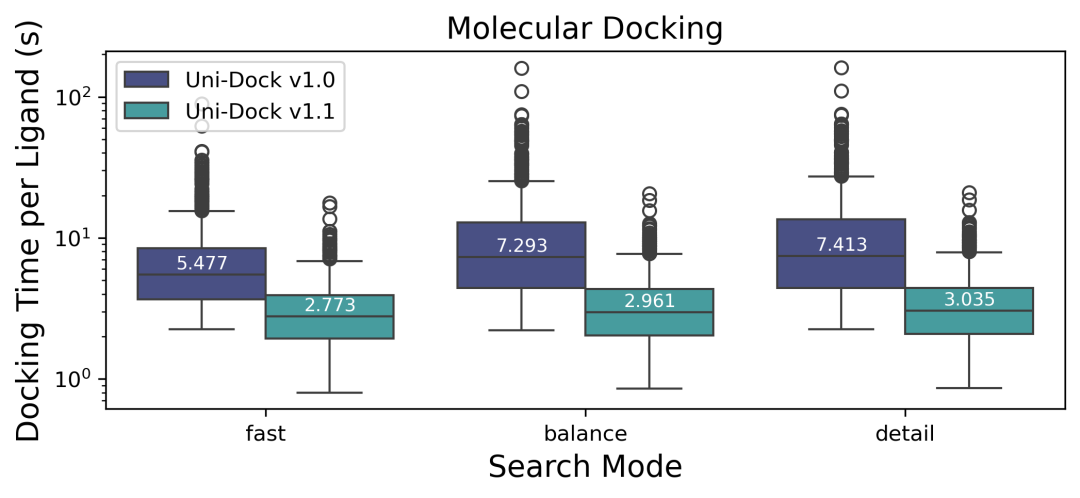
在基准测试机型上,Uni-Dock v1.1 的单分子对接速度分别是 fast 模式下 2.773s/ligand(提升 194%),balance 模式下 2.961s/ligand(提升 246%),detail 模式下 3.035s/ligand(提升 244%)。
虚拟筛选特指一批配体分子向单个受体蛋白的对接计算过程,常常用于虚拟分子库面向特定受体蛋白的快速筛选评估,以获得对该受体蛋白具有潜在活性的配体分子。在 Uni-Dock v1.1 版本中,虚拟筛选的主要提升如下: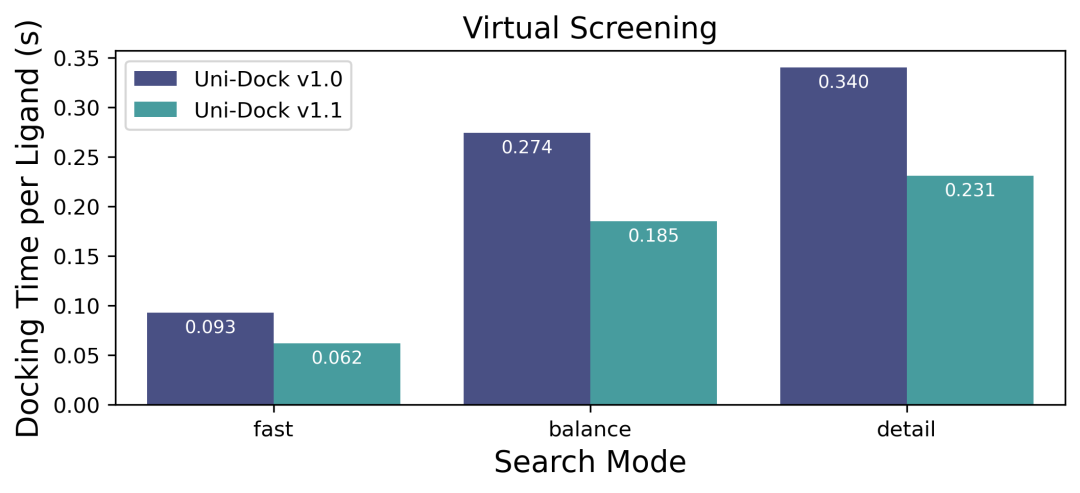
在基准测试机型上,Uni-Dock v1.1 的虚拟筛选速度分别是 fast 模式下 0.062s/ligand(提升 150%),balance 模式下 0.185s/ligand(提升 148%),detail 模式下 0.231s/ligand(提升 147%)。Uni-Dock v1.1 为计算能力(compute capability)更高的 NVIDIA GPU 开展了进一步的适配,在最新消费级旗舰 GPU 上,虚拟筛选的速度能稳定达到 fast 模式 0.030s/ligand,balance 模式 0.067s/ligand,detail 模式 0.082s/ligand。现在,使用 Uni-Dock v1.1 fast 模式开展 1 亿分子的大规模虚拟筛选,100 卡 GPU 集群最快只需要运行 8.3 个小时就能完成全部任务。我们发布了 Uni-Dock Tools 分子对接工具包,给广大用户提供了更好的使用体验和优秀的实践案例。
Uni-Dock Tools 整合了受体蛋白准备工具 proteinprep 和配体分子准备工具 ligandprep 等实用工具,补全了 Uni-Dock 使用过程中的前置文件处理方法。Uni-Dock Tools 还整合了 unidock-pipeline 分子对接工作流,能够接受主流格式的受体蛋白和配体分子文件作为输入,并自动执行 proteinprep 和 ligandprep 进行准备工作。
Uni-Dock Tools 和 Uni-Dock v1.1 的使用案例可见:
https://nb.bohrium.dp.tech/detail/48759512168
Uni-Dock Tools 中还收录了基于 Uni-Dock 开发的多构象对接方法(Multi-Conformation Dock,MCDock)。MCDock 充分利用 Uni-Dock 的快速对接能力,通过大量的构象枚举、多构象刚性对接、优秀构象的局部优化,来可以进一步提升对受体蛋白-配体分子复合物结合构象的采样空间覆盖率,来获得更为准确的复合物构象。https://nb.bohrium.dp.tech/detail/91221652314 https://github.com/dptech-corp/Uni-Dock/tree/main/unidock_tools获取分子对接工具包的最新版本。
为了在统一标准下评估软件性能和精度,我们整理并发布了 Uni-Dock 使用的基准数据集 Uni-Dock Benchmarks。Uni-Dock Benchmarks 以公开数据集或文献数据为基础整理,面向 Uni-Dock 的适用场景对原始数据进行了清洗,目前包含分子对接基准数据集3个(含有 84 个复合物体系的 Astex 数据集、含有 271 个复合物体系的 CASF-2016 数据集和含有 428 个复合物体系的 PoseBuster 数据集),以及虚拟筛选基准数据集5个(含有 824 个配体分子的 D4 数据集、含有 824 个配体分子的 sigma2 数据集、含有 3580 个配体分子的 NSP3 数据集、含有 7321 个配体分子的 PPARG 数据集和含有 458491 个配体分子的 GBA 数据集)。 https://github.com/dptech-corp/Uni-Dock-BenchmarksUni-Dock 作为 DeepModeling 社区的孵化软件,依照 LGPL 协议开放源代码。我们欢迎广大用户使用并提出问题、建议和需求,亦欢迎开源社区开发者共同参与 Uni-Dock 的优化升级。为了便于开源社区开发者的协同,我们在此次版本更新中一并发布了社区建设的相关文档。如果您遇到了安装、使用上的问题,或是希望 Uni-Dock 增加一个新的特性,请向 Uni-Dock 的 GitHub 仓库提交一个新的 issue,根据 issue 表单的指引提供必要信息;如果您希望为 Uni-Dock 贡献新功能,欢迎按照贡献指南更新代码。具体如下:1. 提交issue:
https://github.com/dptech-corp/Uni-Dock-Dev/issues/new2. 贡献指南:
https://github.com/dptech-corp/Uni-Dock-Dev/blob/main/.github/CONTRIBUTING.md3. 代码格式规范:
https://github.com/dptech-corp/Uni-Dock-Dev/blob/main/unidock/.clang-formatUni-Dock 为计算能力(compute capability)为 7.0 及以上的 NVIDIA GPU 提供官方支持。
软件测试有助于发现开发过程中的潜在问题,确保计算的精度与速度符合预期;自动化的部署流程能帮助用户及开发者更便捷地评估最新开发版本;充分的测试体系可以为用户和开发者建立对软件的信任,促进社区成员的协同合作,并帮助开发者实践良好的开发流程。作为开源软件,Uni-Dock 持续完善测试用例及测试框架,做好迎接更多合作者的准备。此次版本发布,我们完善了 Uni-Dock 及 Uni-Dock Tools 的测试框架,加入了新的单元测试及集成测试用例;基于 GitHub Actions 的工作流会在新 PR 被接收时构建新的 Docker 镜像并发布至 Docker Hub:
dptechnology/unidock;
dptechnology/unidock_tools。以下为各位贡献者的 GitHub ID(依照字母顺序排列)。@caic99 @envidian @Hong-Rui @hypnopump @lucifer1004 @pkuyyj @prabindh @rongfengzou @UR-Free @ysyecust @YNYuan @zhangjingrong @zhengh96 @zmsunnyday
https://github.com/dptech-corp/Uni-Dock/https://app.bohrium.dp.tech/uni-dock/
[1] Yu, Y., Cai, C., Wang, J., Bo, Z., Zhu, Z., & Zheng, H. (2023). Uni-dock: Gpu-accelerated docking enables ultralarge virtual screening. Journal of Chemical Theory and Computation, 19(11), 3336-3345.深势科技是“AI for Science”科学研究范式的引领者和践行者,致力于运用人工智能和多尺度的模拟仿真算法,结合先进计算手段求解重要科学问题,为人类文明最基础的生物医药、能源、材料和信息科学与工程研究打造新一代微尺度工业设计和仿真平台。我们开创性地提出了「多尺度建模+机器学习+高性能计算」的革命性科学研究新范式,并推出了Bohrium®科研云平台、Hermite®药物计算设计平台、RiDYMO®难成药靶标研发平台及 Piloteye®电池设计自动化平台等工业设计与仿真基础设施,颠覆了现有研发模式,打造“计算引导实验、实验优化设计”的全新范式。深势科技是国家高新技术企业、国家专精特新“小巨人”企业,总部位于北京,并在上海、深圳等城市布局研发中心。科研技术团队由中国科学院院士领衔,汇集了超百位数学、物理、化学、生物、材料、计算机等多个领域的优秀青年科学家和工程师,其中公司的博士及博士后占比超过35%。核心成员获得过2020年全球计算机高性能计算领域的最高奖项“戈登贝尔奖”,相关工作当选2020年中国十大科技进展和全球AI领域十大技术突破。
内容中包含的图片若涉及版权问题,请及时与我们联系删除




















评论
沙发等你来抢