DRUGONE
空间转录组技术为在组织原位解析基因表达提供了重要手段,但如何将二维切片数据整合为三维结构仍然是核心挑战。空间对齐,即基于空间坐标和基因表达信息对多个组织切片进行配准,是实现这一目标的关键步骤。然而,尽管近年来涌现了多种对齐方法,针对其性能的系统性评估仍然缺乏。
在本研究中,研究人员构建了一个全面的基准评估框架,对多种主流空间对齐方法进行系统比较。通过在不同数据集和技术平台上执行295项对齐任务,研究人员从准确性、效率、鲁棒性、易用性以及对下游分析的影响等多个维度进行评估。结果表明,现有方法在复杂真实场景中仍存在显著局限。针对这些问题,研究人员进一步提出了有效的优化策略,并总结了实用指南,帮助研究人员根据数据特征选择合适的方法并优化分析流程。该研究为空间对齐算法的发展和应用提供了系统性参考框架。

空间转录组技术能够同时获取基因表达信息与空间位置信息,使研究人员可以在组织原位解析基因表达模式。这些技术主要分为测序型和成像型两类,尽管技术路径不同,但大多数仍基于二维组织切片进行测量。
然而,生物组织本质上是三维结构,仅依赖单个二维切片会丢失重要空间信息。因此,将多个切片整合至统一坐标系中,实现三维重建,成为空间生物学的重要目标。空间对齐正是实现这一目标的关键步骤,它通过整合多张切片数据,恢复更完整的组织结构信息。
尽管医学影像配准领域为这一问题提供了重要启发,但空间转录组数据具有自身特性,例如表达稀疏性、不同平台分辨率差异以及组织间生物异质性等,使得传统方法难以直接应用。此外,不同数据场景(如切片重叠程度、旋转偏差等)也进一步增加了对齐难度。
已有研究虽对部分方法进行了评估,但缺乏针对空间对齐问题的系统性基准分析,尤其是在跨平台、大规模数据和真实复杂场景下的表现仍不清晰。因此,研究人员开展了本研究,以填补这一关键空白。
方法
研究人员收集并整理了来自多种空间转录组平台的数据,构建了包含240个真实切片和35组模拟切片的数据集,共形成295项对齐任务。所有数据统一预处理,以保证不同方法之间的公平比较。
在此基础上,研究人员设计了一个多维度评估框架,从六个方面系统评价方法性能,包括对齐准确性、计算效率、鲁棒性、对下游任务的影响、复杂应用场景表现以及方法易用性。准确性通过基因表达相似性和区域匹配程度进行量化;效率通过运行时间与内存消耗评估;鲁棒性通过人为扰动(如旋转与重叠变化)测试;同时还评估对齐结果对三维空间聚类等下游任务的影响。
此外,研究人员还特别关注实际应用中的挑战场景,例如多连续切片、跨平台数据以及大规模数据处理,并提出针对性的优化策略。
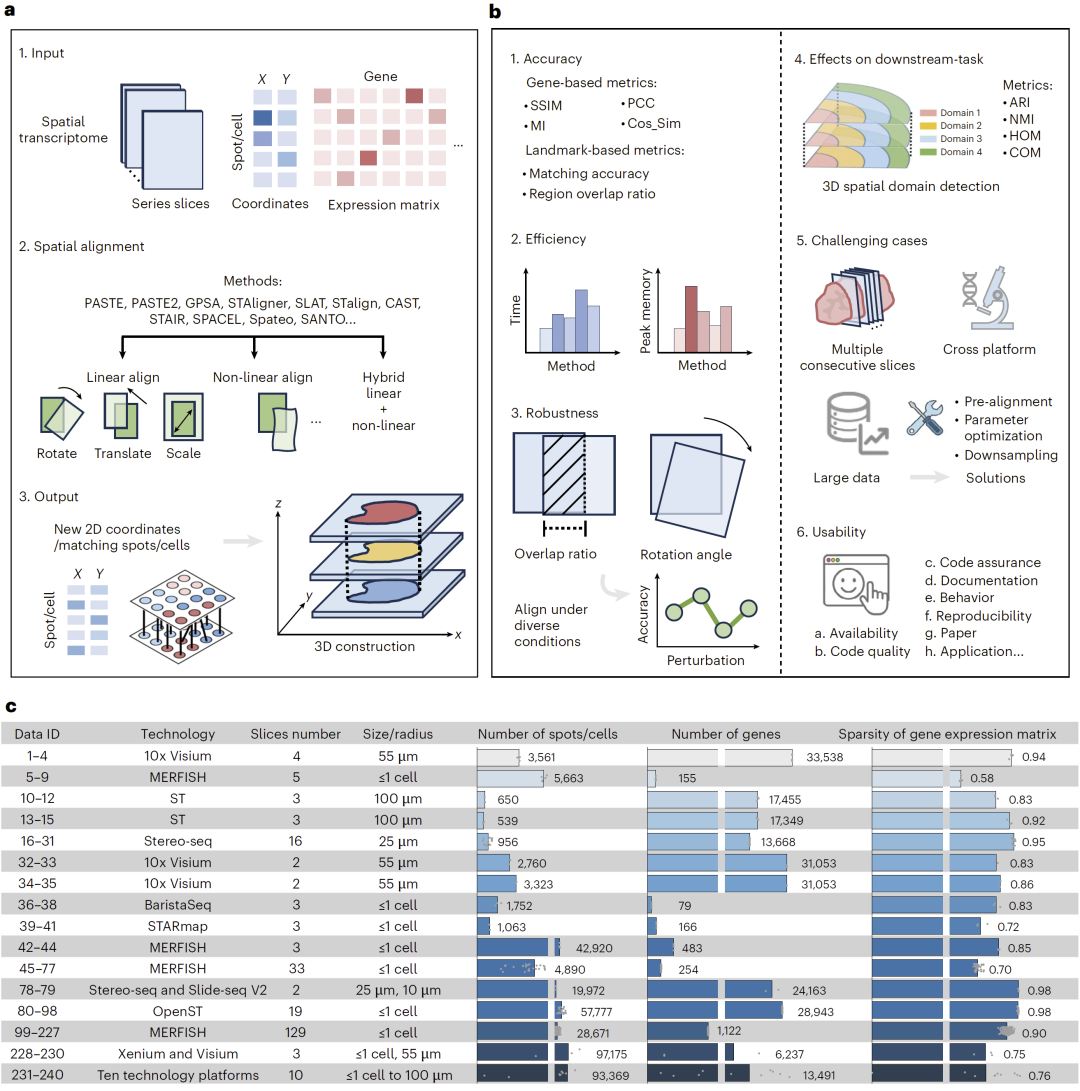
图1:基准评测流程、方法与数据集概览。
结果
基准框架与方法整体概览
研究人员比较了11种主流空间对齐方法,这些方法大多以基因表达矩阵和空间坐标为输入,通过线性、非线性或混合变换实现切片对齐。最终输出通常为新的空间坐标或匹配点对,并将多个切片整合至统一三维空间。
评估数据涵盖多种技术平台,包括Visium、MERFISH、Stereo-seq、STARmap等,确保方法在不同分辨率、数据规模和生物场景下的表现均得到检验。
常规场景下的方法表现
在常规场景中,研究人员首先在单一技术、小规模数据上评估方法性能。结果显示,不同方法在不同技术平台上的表现存在显著差异。
在测序型数据(如Visium)中,一些方法表现稳定且准确,而在成像型数据(如MERFISH)中,另一些方法则更具优势。这表明方法性能具有明显的技术依赖性。
此外,多种评价指标之间表现出较高一致性,说明评估体系具有可靠性,但部分指标之间也存在差异,提示不同指标捕捉了对齐性能的不同方面。
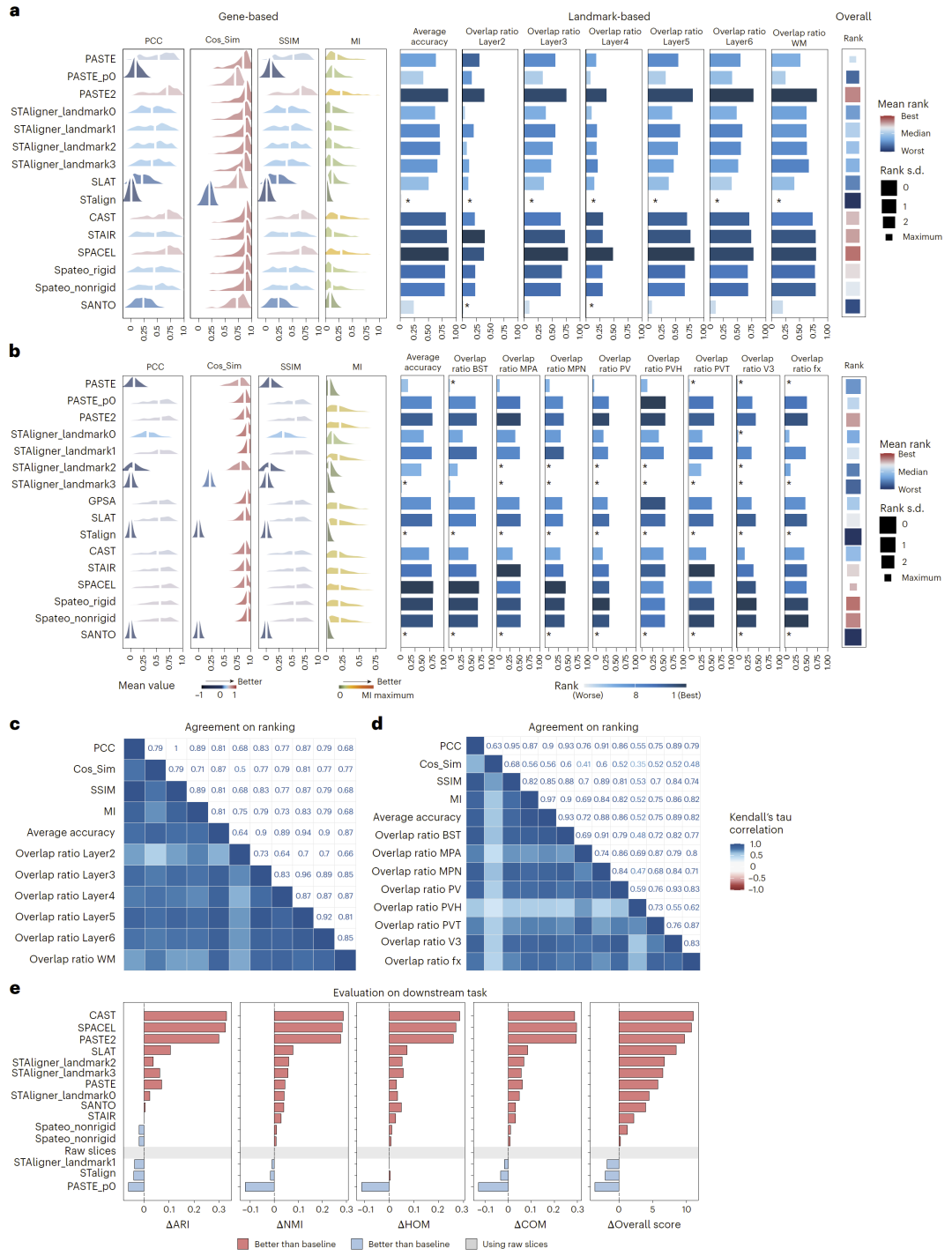
图2:常规场景下的性能评估及其对下游任务的影响。
对下游任务的影响
研究人员进一步分析了对齐方法对下游分析的影响,特别是三维空间聚类任务。结果显示,大多数对齐方法均显著提升了下游分析性能。
表现最佳的方法在多个评价指标上均明显优于未对齐数据,表明高质量的空间对齐对于后续生物学分析至关重要。因此,在实际分析流程中,应优先选择高性能对齐方法,以提升整体分析质量。
鲁棒性分析
在鲁棒性评估中,研究人员通过模拟不同重叠比例和旋转角度来测试方法稳定性。
结果表明,大多数方法在切片重叠较高时表现更好,而部分方法对初始旋转角度较为敏感。相比之下,一些方法在不同条件下均保持较高稳定性,表现出更强的泛化能力。
此外,当切片旋转角度较小(如±30°)时,对齐效果通常更佳。这说明实际应用中合理预处理数据可以显著提升对齐性能。
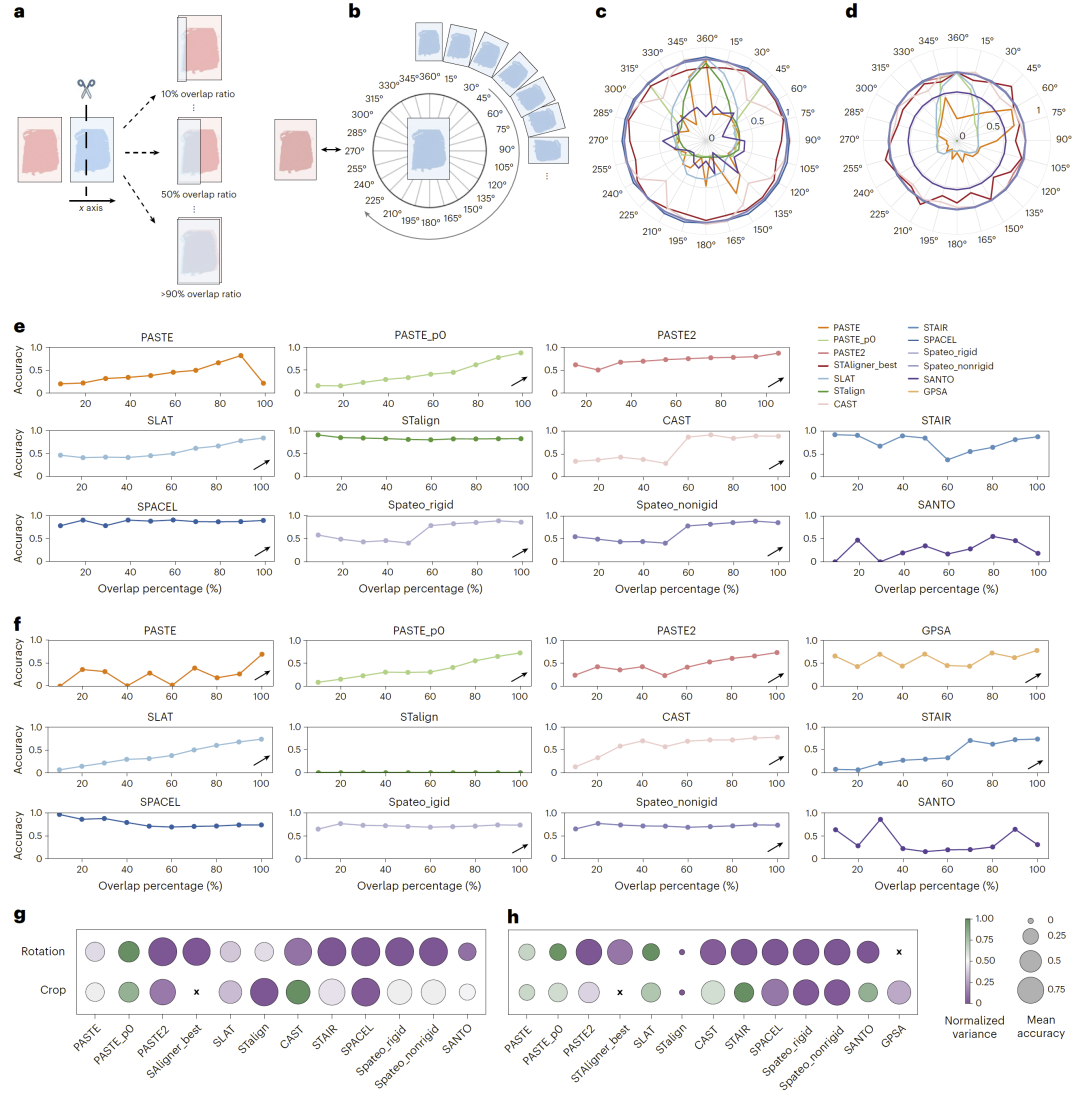
图3:扰动条件下的鲁棒性评估。
综合性能与易用性
研究人员进一步从整体角度评估方法性能,包括不同数据类型下的表现以及工具的可用性。
结果显示,不同方法在准确性、效率和可扩展性之间存在权衡。有些方法精度较高但计算开销较大,而另一些方法则更高效但精度略低。同时,工具的代码质量、文档完善程度和可复现性也存在明显差异。
因此,在实际应用中,方法选择应综合考虑数据规模、分析目标以及计算资源。

图4:整体性能与方法易用性总结。
复杂场景下的挑战与改进策略
在更接近真实应用的复杂场景中(如多切片连续对齐、跨平台整合和大规模数据处理),研究人员发现现有方法普遍存在性能下降和计算资源消耗过高的问题。
为解决这些瓶颈,研究人员提出了多种优化策略,包括预对齐、参数优化和数据下采样等方法。这些策略可以单独或组合使用,以提高方法在复杂场景中的适用性。
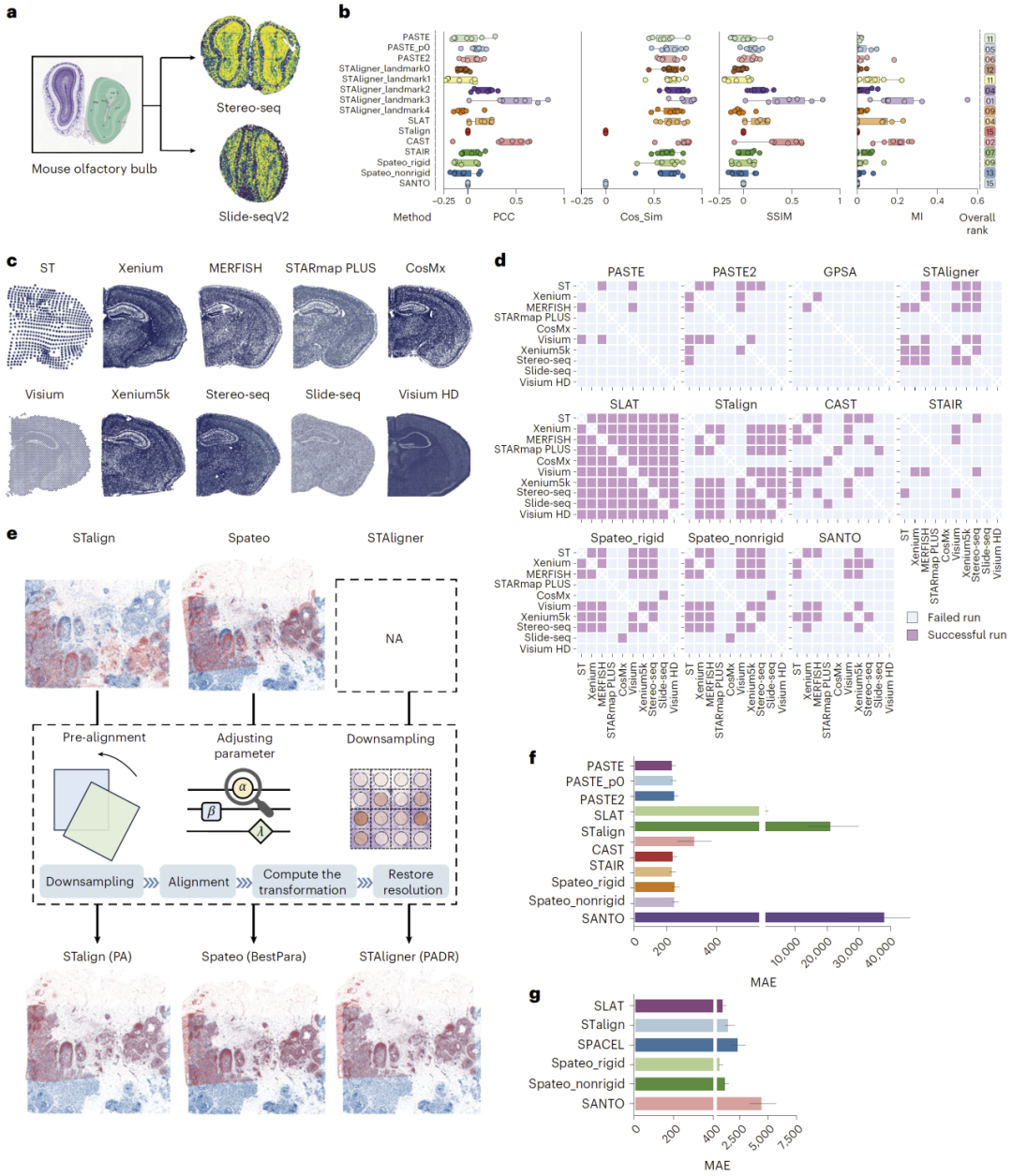
图5:复杂应用场景分析:跨平台、多连续切片与大规模数据。
讨论
本研究系统评估了空间转录组数据对齐方法的性能,并揭示了不同方法在多种场景下的优势与局限。研究结果表明,尽管已有方法在常规任务中表现良好,但在复杂真实应用中仍面临诸多挑战,例如鲁棒性不足和计算成本过高。
此外,对齐质量对下游分析具有显著影响,这强调了在分析流程中选择合适对齐方法的重要性。研究人员提出的优化策略为提升方法性能提供了可行路径,也为未来方法开发指明了方向。
随着空间转录组技术的快速发展,数据规模和复杂性将持续增加。本研究提供的基准框架具有良好的扩展性,可用于评估新方法和新数据,为该领域持续发展提供重要支撑。
整理 | DrugOne团队
参考资料
Yan, Y., Gu, T., Sun, C. et al. Benchmarking alignment methods for spatial transcriptomics data. Nat Comput Sci (2026).
https://doi.org/10.1038/s43588-026-00977-z

内容为【DrugOne】公众号原创|转载请注明来源
内容中包含的图片若涉及版权问题,请及时与我们联系删除



评论
沙发等你来抢