【论文标题】Deep graph learning of inter-protein contacts
【作者团队】Ziwei Xie, Jinbo Xu
【发表时间】2021/08/15
【机 构】芝加哥丰田计算技术研究所
【论文链接】https://journals.plos.org/ploscompbiol/article?id=10.1371/journal.pcbi.1009284
【推荐理由】预训练语言模型和图神经网络的多模态联用
蛋白质间(界面)接触预测对于蛋白质-蛋白质相互作用的虚拟结构表征非常有用。尽管深度学习已经被应用到这个问题上,但其准确性不如蛋白内接触预测好。本文提出了一种新的深度学习方法GLINTER,用于二聚体的界面接触预测,利用了蛋白质三级结构的旋转不变表征和多重序列比对的预训练语言模型。CASP-CAPRI数据集上测试,GLINTER在同源二聚体上实现的平均最高L/10精度为54.35%,在所有二聚体上为51.56%,远远高于最新深度学习方法DeepHomo在同源二聚体上获得的30.43%和BIPSPI在所有二聚体上获得的14.69%。我们的实验表明,GLINTER预测的接触有助于改善对接诱饵的选择,适用于蛋白质组尺度的蛋白质-蛋白质相互作用和复合物的研究。
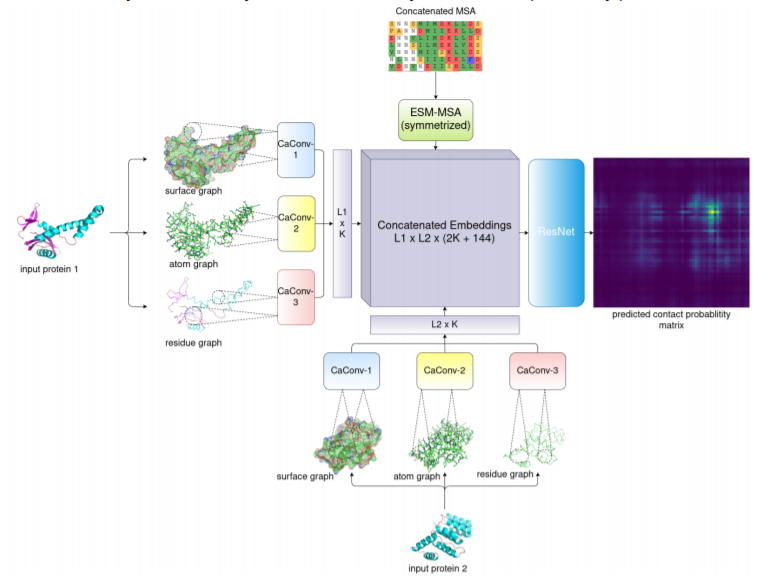
上图GLINTER模型的框架,由两个主要模块组成:一个孪生图卷积网络(GCN)和一个16块的ResNet。GCN从来自单体结构的3种类型(表面,原子,残基)的图形中提取局部特征。ResNet将GCN模块的输出和MSA Transformer产生的注意力权重作为输入,并产生界面接触预测。
MSA transformer:使用行注意力权重作为界面共进化的信号。作者使用RaptorX-ComplexContact提出的protocol为异质二聚体建立一个联合MSA;对于一个同源二聚体,我们简单地将MSA中的每个序列与自身连接起来。最终从联合MSA中选择一组不同的序列作为MSA transformer的输入。
残基图:一个节点是由其CA原子代表的残基,当且仅当它们的CA原子之间的欧氏距离在某个阈值内时,两个残基节点之间有一条边。
原子图:一个节点是一个重原子或由其CA原子代表的残基,当且仅当它们的欧氏距离在一定的阈值内时,一个残余物节点和一个原子节点之间有一条边。
表面图:使用Reduce、MSMS和trimesh来构建蛋白质结构的三角形网,即一个包围蛋白质的网状结构。表面中的两个相邻的三角形共享一条边或至少一个顶点,在表面图中,一个节点代表一个残基或三角表面的一个顶点。我们在一个残基节点和一个三角形顶点之间添加一条边,当且仅当它们的欧氏距离在某个阈值之内。建立一个表面图只需要几秒钟,因此,我们的方法在大规模预测上有很好的扩展性。相比之下,DeepHomo使用计算密集型的对接程序来生成对接图。
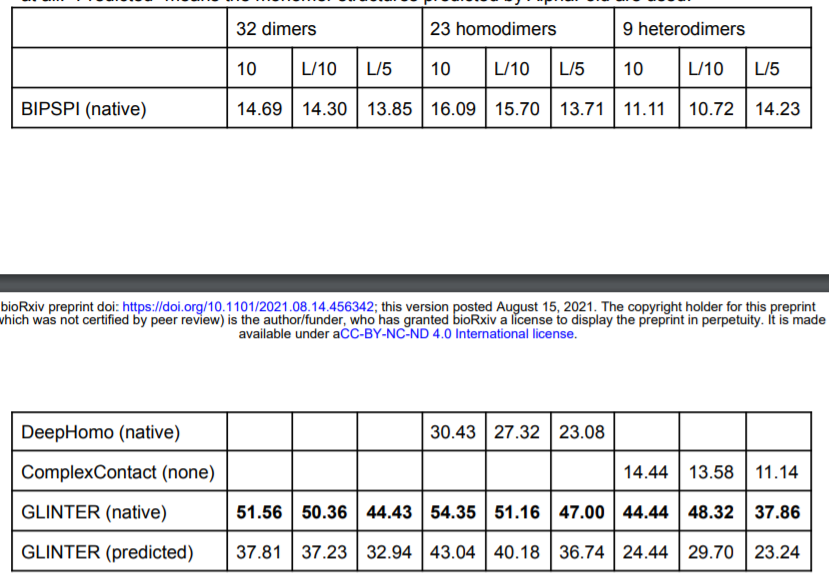
如上图所示,在23个测试上,GLINTER有54.35%的前10位精度和51.16%的前L/10精度,而DeepHomo有30.43%的前10位精度和27.32%的前L/10精度。在9个异源二聚体上测试,GLINTER有44.44%的前10位精度和48.32%的前L/10精度,而ComplexContact有14.44%的前10位精度和13.58%的前L/10精度。即使使用AlphaFold-2预测的单体结构(predicted)作为输入,GLINTER在同源二聚体上有43.04%的前10位精度,在异源二聚体上有24.44%的前10位精度。总之,无论使用的是实验性单体结构还是预测性单体结构,GLINTER都比DeepHomo和ComplexContact高出很多。
内容中包含的图片若涉及版权问题,请及时与我们联系删除



评论
沙发等你来抢